Enbaspolymorfi
| Den här artikeln behöver fler eller bättre källhänvisningar för att kunna verifieras. (2019-12) Åtgärda genom att lägga till pålitliga källor (gärna som fotnoter). Uppgifter utan källhänvisning kan ifrågasättas och tas bort utan att det behöver diskuteras på diskussionssidan. |
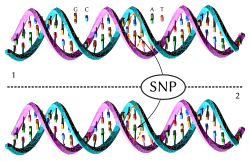
Enbaspolymorfi (eng. Single Nucleotide Polymorphism, SNP och ofta uttalat som "snipp"), är en positionsbestämd variation i arvsmassan som berör en enda nukleotid. Till exempel kan DNA-sekvensen AATGCC vara förändrad till AACGCC. En mutation som har uppstått i könscellernas DNA och överlever i populationen kallas för SNP om den endast berör en position i DNA-sekvensen, medan den kallas STR om den utgörs av ett förändrat antal upprepningar av en DNA-sekvens.
SNP:er kan, men behöver inte, ge förändringar i aminosyrasekvensen i kodande gener på grund av att flera tripletter kan koda för samma aminosyra. Därför behöver inte polymorfin ha betydelse för fenotypen. Om däremot variationen ligger inom ett funktionellt avsnitt av DNA kan den ge effekter på till exempel metabolism av läkemedel och mottaglighet för sjukdomar.
Forskare har börjat studera SNP:er i avsikt att hitta variationer som är länkade till sjukdomar, men de är även användbara för populationsgenetiska studier, exempelvis i GWAS-studier med hjälp av SNP-mikromatrisanalys.
Människan[redigera | redigera wikitext]
Människans DNA har ungefär 3 miljarder nukleotider. De flesta är identiska mellan alla människor, men ungefär en av tusen varierar mellan olika individer till följd av mutationer - antingen SNP:er eller STR:er. SNP:er får beteckningar efter vilka forskare eller laboratorier som har hittat dem. Typiska namn på SNP:er hos människan är till exempel M253, L1302, CTS4179, YP408 och Z18.[1]
Vid genetisk släktforskning delas människan in i två hierarkiska träd av haplogrupper, vars förgreningar definieras av SNP:er som har inträffat i Y-kromosomen (YDNA, som söner ärver på fädernet), respektive i mitokondriellt DNA (mtDNA, som både en son och en dotter ärver på mödernet). Varje individ har således en MtDNA-haplotyp, som definieras av den sekvens av SNP:er som har inträffat i MtDNA längs personens morslinje (släktlinje via mor, mormor, morsmors mor, och så vidare). En man har dessutom en YDNA-haplotyp, som definieras av den sekvens av SNP:er som har inträffat i Y-kromosomen längs farslinjen. En haplogrupp är en grupp av bestående av haplotyper som har gemensam genetisk historia. En haplogrupp kan namnges utifrån definierande SNP, det vill säga den senast inträffade SNP:en som har inträffat längs farslinjen respektive morslinjen som förenar alla som tillhör denna haplogrupp. Ett exempel är YDNA-haplogruppen I-M253, som är vanlig bland svenska män, och som är en förgrening inom YDNA-haplogruppen I. Den senast inträffade SNP som förenar alla män som tillhör I-M253 är M253 i Y-kromosomen. I-M253 kan även betecknas I1, det vill säga förgrening nummer 1 av haplogrupp I.
Y-kromosomens DNA-sekvens är många gånger längre än det mitokondriella DNA:t. Ett komplett YDNA-test testar hundratusentals SNP:er i Y-kromosomen, och ger exakt YDNA-haplotyp.[1] Enklare och billigare YDNA-tester kartlägger istället ett litet antal STR:er, och utifrån dessa kan YDNA-haplogruppen uppskattas, men inte exakt haplotyp. Det finns även DNA-test för specifika SNP:er, i syfte att komplettera och förfina resultat från STR-baserade test. Att kombinera ett STR-baserat test med tester av specifika SNP:er kan vara mindre kostsamt än fullständigt YDNA-test för att ta reda på individens haplotyp, men ger inte samma möjlighet att upptäcka tidigare okända förgreningar av YDNA-haploträdet.
Källor[redigera | redigera wikitext]
- ^ [a b] Karin Bojs; Peter Sjölund. Svenskarna och deras fäder - de senaste 11 000 åren (Andra tryckningen). sid. 213-214. ISBN 9789100167547. OCLC 973876808
| |||||||||||||||||
